
Citation: XU Xiejun, XIAO Xingqing, XU Shouhong, LIU Honglai. Computational Study of Thermosensitivity of Liposomes Modulated by Leucine Zipper-Structured Lipopeptides[J]. Acta Physico-Chimica Sinica, 2019, 35(6): 598-606. doi: 10.3866/PKU.WHXB201806034

亮氨酸拉链型脂肽对脂质体温敏性调节的分子模拟
English
Computational Study of Thermosensitivity of Liposomes Modulated by Leucine Zipper-Structured Lipopeptides
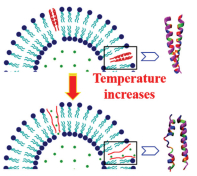
-
-
[1]
Aschenbrenner, D. S. Am. J. Nurs. 2017, 117, 22. doi: 10.1097/01.NAJ.0000521967.00600.3a
-
[2]
Liehr, T. Eur. J. Hum. Genet. 2017, 25, 902. doi: 10.1038/ejhg.2017.7
-
[3]
Lokerse, J. M.; Eggermont, M. M.; Grüll, H.; Koning, G. A. J. Controll. Release 2018, 270, 282. doi: 10.1016/j.jconrel.2017.12.012
-
[4]
Mura, P.; Matascia, N.; Nativi, C.; Richichi, B. Eur. J. Pharm. Biopharm. 2018, 122, 54. doi: 10.1016/j.ejpb.2017.10.008
-
[5]
Malaescu, I.; Fannin, P. C.; Marin, C. N.; Lazic, D. Med. Hypotheses 2018, 110, 76. doi: 10.1016/j.mehy.2017.11.004
-
[6]
Al-Ahmady, Z. S.; Al-Jamal, W. T.; Bossche, J. V.; Bui, T. T.; Drake, A. F.; Mason, A. J.; Kostarelos, K. ACS Nano 2012, 6, 9335. doi: 10.1021/nn302148p
-
[7]
Srinivasan, M.; Lahiri, D. K. Mol. Neurobiol. 2017, 54, 8063. doi: 10.1007/s12035-016-0277-5
-
[8]
Roodbarkelari, F.; Groot, E. P. New Phytol. 2017, 213, 95. doi: 10.1111/nph.14132
-
[9]
Wang, S. J.; Shen, Y. X.; Zhang, J. Q.; Xu, S. H.; Liu, H. L. Phys. Chem. Chem. Phys. 2016, 18, 10129. doi: 10.1039/C6CP00378H
-
[10]
Wang, S. J.; Han, X.; Liu, D. Y.; Li, M. Y.; Xu, S. H.; Liu, H. L. Langmuir 2017, 33, 1478. doi: 10.1021/acs.langmuir.6b04080
-
[11]
王斯佳, 李梦雅, 徐首红, 刘洪来.物理化学学报, 2017, 33, 829. doi: 10.3866/PKU.WHXB201701062Wang, S. J.; Li, M. Y.; Xu, S. H.; Liu, H. L. Acta Phys. -Chim. Sin. 2017, 33, 829. doi: 10.3866/PKU.WHXB201701062
-
[12]
Xu, X. X.; Xiao, X. Q.; Xu, S. H.; Liu, H. L. Phys. Chem. Chem. Phys. 2016, 18, 25465. doi: 10.1039/C6CP05145F
-
[13]
Cornell, W. D.; Cieplak, P.; Bayly, C. I.; Kollmann, P. A. J. Am. Chem. Soc. 1993, 115, 9620. doi: 10.1021/ja00074a030
-
[14]
Cornell, W. D.; Cieplak, P.; Bayly, C. I.; Gould, I. R.; Merz, K. M.; Ferguson, D. M.; Spellmeyer, D. C.; Fox, T.; Caldwell, J. W.; Kollman, P. A. J. Am. Chem. Soc. 1995, 117, 5179. doi: 10.1021/ja00124a002
-
[15]
Cieplak, P.; Cornell, W. D.; Bayly, C. I.; Kollmann, P. A. J. Comput. Chem. 1995, 16, 1357. doi: 10.1002/jcc.540161106
-
[16]
Abraham, M. J.; Murtola, T.; Schulz, R.; Pll, S.; Smith, J. C.; Hess, B.; Lindahl, E. SoftwareX 2015, 1–2, 19. doi: 10.1016/j.softx.2015.06.001
-
[17]
Pronk, S.; Pall, S.; Schulz, R.; Larsson, P.; Bjelkmar, P.; Apostolov, R.; Shirts, M. R.; Smith, J. C.; Kasson, P. M.; van der Spoel, D.; et al. Bioinformatics 2013, 29, 845. doi: 10.1093/bioinformatics/btt055
-
[18]
Maier, J.; Martinez, C.; Kasavajhala, K.; Wickstrom, L.; Hauser, K.; Simmerling, C. J. Chem. Theory Comput. 2015, 11, 3696. doi: 10.1021/acs.jctc.5b00255
-
[19]
Onufriev, A.; Bashford, D.; Case, D. A. Proteins: Struct., Funct., Bioinf. 2004, 55, 383. doi: 10.1002/prot.20033
-
[20]
Martínez, L.; Andrade, R.; Birgin, E. G.; Martínez, J. M. J. Comput. Chem. 2009, 30, 2157. doi: 10.1002/jcc.21224
-
[21]
Martínez, J. M.; Martínez, L. J. Comput. Chem. 2003, 24, 819. doi: 10.1002/jcc.10216
-
[22]
Biasini, M.; Bienert, S.; Waterhouse, A.; Arnold, K.; Studer, G.; Schmidt, T.; Kiefer, F.; Cassarino, T. G.; Bertoni, M.; Bordoli, L.; et al. Nucleic Acids Res. 2014, 42, 252. doi: 10.1093/nar/gku340
-
[23]
Kiefer, F.; Arnold, K.; Künzli, M.; Bordoli, L.; Schwede, T. Nucleic Acids Res. 2009, 37, 387. doi: 10.1093/nar/gkn750
-
[24]
Arnold, K.; Bordoli, L.; Kopp, J.; Schwede, T. Bioinformatics 2006, 22, 195. doi: 10.1093/bioinformatics/bti770
-
[25]
Dickson, C. J.; Madej, B. D.; Skjevik, A. A.; Betz, R. M.; Teigen, K.; Gould, I. R.; Walker, R. C. J. Chem. Theory Comput. 2014, 10, 865. doi: 10.1021/ct4010307
-
[26]
Jorgensen, W. L.; Chandrasekhar, J.; Madura, J. D.; Impey, R. W.; Klein, M. L. J. Chem. Phys. 1983, 79, 926. doi: 10.1063/1.445869
-
[27]
Altis, A.; Nguyen, P. H.; Hegger, R.; Stock, G. J. Chem. Phys. 2007, 126, 244111. doi: 10.1063/1.2746330
-
[28]
Borgohain, G.; Paul, S. Mol. Simul. 2017, 43, 52. doi: 10.1080/08927022.2016.1233546
-
[29]
Kabsch, W.; Sander, C. Biopolymers 1983, 22, 2577. doi: 10.1002/bip.360221211
-
[1]
-
 扫一扫看文章
扫一扫看文章
计量
- PDF下载量: 7
- 文章访问数: 961
- HTML全文浏览量: 107

 下载:
下载:

