

Citation: Yu-Xing TAN, Xu-Jian ZHANG, Le CHEN, Fang-Fang MAO, Wu-Jiu JIANG. Syntheses, Antitumor Activity and DNA Interaction of Diphenyltin Complexes Based on Salen-like Ligand[J]. Chinese Journal of Inorganic Chemistry, 2021, 37(10): 1801-1808. doi: 10.11862/CJIC.2021.209

基于类salen配体的二苯基锡配合物的合成、抗肿瘤活性及其与DNA相互作用
English
Syntheses, Antitumor Activity and DNA Interaction of Diphenyltin Complexes Based on Salen-like Ligand
-
Key words:
- organotin complex
- / salen-like ligand
- / antitumor activity
- / DNA
-
0. 引言
自从1965年Rosenberg[1]发现了第一个有效的抗癌金属药物——顺铂以来,具有抗癌活性的金属配合物便吸引了更多的科研人员从事相关研究。有机锡是一类Sn和C原子直接结合所形成的金属有机化合物,由于它具有一定的细胞毒性作用,并且与DNA结合能力较强,能够抑制细胞增殖、诱导细胞凋亡等,因此,该类化合物在癌症化学疗法的相关报道中占有重要地位[2-5]。虽已有许多关于不同有机锡化合物的生物活性和结构的报道[6-8],但科研人员仍很难事先根据药物的化学结构准确预测药物的生物活性。因此,合成大量具有潜在的生物活性的分子并且探索其构效关系,有助于开发新的有机金属抗癌药物。
类salen型酰腙配体对配合物的性质表现出较好的调控作用,其中Ay等[9]报道的二苯乙二酮苯甲酰腙镍配合物具有较好的抗肺癌活性;Srivastava等[10]报道的二苯乙二酮苯甲酰腙钒配合物具有较好的氧化还原活性。众所周知,有机锡配合物中的配体在其几何结构中发挥着至关重要的作用,并影响其生物活性[11-15]。二苯基二氯化锡由于其脂溶性过高,成药性低,所以我们试图通过类salen型酰腙配体来调控二苯基锡配合物的脂水分配系数,从而提高此类有机锡配合物的成药性。同时,本文报道合成的配合物的体外抗癌活性,研究了配合物与DNA的相互作用,为开发新型金属抗肿瘤药物提供了重要的理论基础。
1. 实验部分
1.1 仪器和试剂
IR用日本岛津Prestige-21红外光谱仪(4 000~ 400 cm-1,KBr压片)测定。1H、13C和119Sn NMR用Bruker AVANCE-500核磁共振仪测定。元素分析用PE-2400 Ⅱ元素分析仪测定。晶体结构用Bruker SMART APEX Ⅱ CCD单晶衍射仪测定。紫外可见光谱用日本岛津公司UV-2550型紫外可见光谱仪测定。HRMS用Thermo Scientific LTQ Orbitrap XL(ESI源)测定。荧光光谱用日本日立F-7000荧光光谱仪测定。热重(TG) 和微分热重(DTG) 曲线用德国NETZSCH TG 209 F3热重分析仪测定:空气气氛、加热速度20 ℃ ·min-1、气体流速为20 mL·min-1、40~ 800 ℃。熔点用北京泰克X-4双目体视显微熔点测定仪测定(温度计未经校正)。
配体参考文献方法[16]合成。溴化乙锭(EB)、小牛胸腺DNA、三羟甲基氨基甲烷(Tris)为Sigma-Aldrich公司产品。其它试剂均为分析纯,水为超纯水。Tris-HCl(0.01 mol·L-1)缓冲溶液通过称取一定量Tris用0.1 mol·L-1的盐酸溶液调至pH值为7.40,使用前配制。小牛胸腺DNA的纯度通过比较260和280 nm处的吸光度来确定(A260/A280=1.8~1.9),用所需pH值条件下的缓冲溶液配制,浓度通过测定260 nm处的吸光度计算而得(ε260=6 600 L·mol-1·cm-1),其储备液置于4 ℃保存。溴化乙锭溶液通过称取适量溴化乙锭固体,用pH=7.40的Tris-HCl(0.01 mol· L-1)缓冲溶液配制。
1.2 配合物的合成
配合物的合成路线如图 1所示。于50 mL圆底烧瓶中,加入1 mmol二苯乙二酮苯甲酰腙或二苯乙二酮水杨酰腙、1 mmol二苯基二氯化锡、20 mL甲醇,搅拌回流3 h。冷却,过滤,通过控制溶剂挥发法分别得到2种配合物的淡黄色晶体。
图 1
[(C6H5(O)C=N—N=C(Ph) — (Ph)C=N—N=C (O)—C6H5)2SnPh2(CH3OH)] ·3CH3OH (1):产率71%。m.p. 40~42 ℃(dec)。元素分析(C44H46N4O6Sn)实测值(计算值,%):C,62.53(62.35);H,5.50(5.48);N,6.63 (6.64)。IR(KBr,cm-1):3 055, 1 587, 1 512, 1 479, 1 431,1 358, 1 323, 1 290,1 260,1 173,1 152,1 092,1 069,1 024,999,914,880,733,714,691,627,602,451。1H NMR(500 MHz,CDCl3):δ 8.20(d,J=7.2 Hz,4H),7.74~7.76(m,4H),7.47(d,J=7.5 Hz,2H),7.36(t,J=7.2 Hz,4H),7.34~7.35(m,4H),7.28~7.32(m,12H)。13C NMR (125 MHz, CDCl3):δ 173.95, 148.73, 143.54, 136.13, 134.40, 131.92, 131.59, 130.86, 129.60,129.51,128.88,128.78, 128.15,127.39,50.86。119Sn NMR (Me4Sn,187 MHz, CDCl3): δ -434.56。HRMS(ESI) m/z: C40H30N4O2Sn+ [M-4CH3OH+H]+计算值719.146 35,实测值719.146 00。
[(o-OH—C6H4(O)C=N—N=C(Ph)—(Ph)C=N— N=C(O)—(o-OH—C6H4))2SnPh2(CH3OH)]·CH3OH (2):产率73%。m.p. 84~86 ℃。元素分析(C42H38N4O6Sn) 实测值(计算值,%):C,62.05(61.93);H,4.73(4.72);N,6.92(6.94)。IR(KBr,cm-1):3 597,3 179, 3 049,2 990,2 895,2 791,1 622,1 584,1 524,1 508, 1 481,1 443,1 431,1 360,1 319,1 298,1 279,1 248, 1 229, 1 188, 1 163, 1 113, 1 098, 1 072,1 026.13,1 001,949,916,891,835,806,756,737,708,694,671,619,604,538,496,455,428。1H NMR(500 MHz,CDCl3):δ 11.77(s,2H),8.15(d,J=7.6 Hz,2H),7.74(d,J=6.7 Hz,4H),7.36~7.38(m,14H),7.23(d,J=7.3 Hz,4H),6.88~6.94(s,4H)。13C NMR(125 MHz,CDCl3):δ 174.37, 160.61, 148.89, 142.06, 136.03,135.08,134.28,131.40, 130.52, 130.27, 129.26, 129.22,128.50,119.08,117.40,116.57,50.91。119Sn NMR(Me4Sn,187 MHz,CDCl3):δ -451.08。HRMS(ESI) m/z:C40H30N4O4Sn+ [M-2CH3OH+H]+ 计算值751.136 18,实测值751.136 11。
1.3 晶体结构测定
采用经石墨单色化的Mo Kα射线(λ=0.071 073 nm),以φ~ω扫描方式收集衍射数据。全部数据经Lp因子和多重扫描吸收校正。晶体结构由直接法解出,全部非氢原子坐标在差值Fourier合成中陆续确定,由理论加氢法给出氢原子在晶胞中的位置坐标。对氢原子和非氢原子分别采用各向同性和各向异性热参数进行全矩阵最小二乘法修正,全部结构分析计算工作采用SHELX-97程序完成[17]。
CCDC:2082589,1;2082590,2。
表 1
Complex 1 2 Empirical formula C44H46N4O6Sn C42H38N4O6Sn Formula weight 845.54 813.45 T / K 273(2) 273(2) Crystal system Triclinic Triclinic Space group P1 P1 a / nm 0.968 97(14) 0.937 12(4) b / nm 1.266 41(18) 1.067 84(5) c / nm 1.765 0(3) 2.005 36(10) α / (°) 106.098(4) 101.575(2) β / (°) 93.394(4) 96.289(2) γ / (°) 96.730(4) 102.982(2) Volume / nm3 2.057 1(5) 1.890 40(15) Z 2 2 Dc / (Mg·m-3) 1.365 1.429 Absorption coefficient / mm-1 0.673 0.729 F(000) 872 832 Crystal size / mm 0.48×0.29×0.28 0.48×0.25×0.13 θ range / (°) 2.92~27.55 3.15~27.51 Limiting indices -12 ≤ h ≤ 12, -16 ≤ k ≤ 16, -22 ≤ l ≤ 22 -12 ≤ h ≤ 12, -13 ≤ k ≤ 13, -26 ≤ l ≤ 26 Reflection collected, unique 43 561, 9 500 (Rint=0.026 4) 39 766, 8 644 (Rint=0.030 1) Completeness 0.998 0.996 Max. and min. transmission 0.834 0 and 0.737 1 0.909 9 and 0.720 6 Data, restraint, parameter 9 500, 0, 507 8 644, 0, 487 Goodness-of-fit on F2 1.091 1.060 Final R indices [I>2σ(I)] R1=0.025 6, wR2=0.064 2 R1=0.030 4, wR2=0.067 2 R indices (all data) R1=0.030 8, wR2=0.066 3 R1=0.037 4, wR2=0.069 5 (Δρ)max, (Δρ)min / (e·nm-3) 373, -403 436, -441 1.4 MTT法检测配合物对细胞的毒性作用
将待测药物溶于少量DMSO,用水稀释至所需浓度,保持最终DMSO浓度小于0.1%。NCI-H460、HepG2、MCF7细胞株取自美国组织培养库(ATCC),NCI-H460、HepG2、MCF7细胞株用含10% 胎牛血清的RPMI 1640(GIBICO公司)培养基,在体积分数5% 的CO2、37 ℃和饱和湿度的培养箱内进行体外培养。体外抗癌药敏试验是通过MTT法测定。数据处理使用Graph Pad Prism version 7.0程序,化合物的IC50通过程序中具有S形剂量响应的非线性回归模型进行拟合得到。
1.5 紫外可见光谱研究
将配合物用DMSO配制成1 mmol·L-1储备液。在5 mL容量瓶中分别加入配合物溶液(50 μmol·L-1) 及不同浓度的ct-DNA(0~100 μmol·L-1),用Tris-HCl缓冲溶液定容,混匀,25 ℃下放置3.0 h,以不同浓度的ct-DNA溶液为参比,分别扫描230~800 nm范围内的紫外可见吸收光谱。
1.6 荧光猝灭作用
将配合物用DMSO配制成1 mmol·L-1储备液。在5 mL容量瓶中分别加入ct-DNA、EB及不同浓度的配合物溶液,用Tris-HCl缓冲溶液定容,混匀,25 ℃下放置3.5 h,分别扫描荧光光谱,激发波长为258 nm,测定540~700 nm波长范围内的荧光光谱,激发和发射光谱扫描狭缝宽度均为5.0 nm。
2. 结果与讨论
2.1 谱学研究
在配合物1、2的红外谱图中,2个配合物在1 587、1 583 cm-1处的吸收峰归属为酰腙(C=N—N=C)键的特征吸收[16, 18-19]。此外,1、2配位键的特征峰ν(Sn—O)、ν(Sn—N)和ν(Sn—C)与文献[20-23]报道的类似化合物的出峰位置一致,由此表明2个目标配合物的生成。
在1H NMR谱中,配合物各组峰的积分面积之比与预期结构的各组质子数相对吻合[24-25]。从谱图中可以看到,配合物1和2中芳环上氢分别在δ= 7.25~8.21和δ =6.88~8.16呈现出多组峰。不同的是,在配合物2中,二苯乙二酮水杨酰腙配体上羟基氢在δ=11.77处呈现一个单峰。对比2个配合物的1H NMR谱图,2个配合物的氢峰基本保持一致,说明2个配合物具有相似的最简结构单元。
在13C NMR谱中,配合物各组峰与理论推测结构碳原子数相吻合[24-25],配合物1和2的特征峰为酰胺键上的碳原子分别在δ=173.95和174.37处的峰,其他碳原子的出峰位置与X射线单晶衍射所得结构均一一对应。
在119Sn NMR谱中,1和2分别在δ=-434.56和-451.08处呈现一个单峰,表明2个配合物中均仅存在一种Sn。
2.2 晶体结构
配合物1、2的主要键长和键角数据列于表 2,分子结构见图 2、3。配合物1和2具有类似结构的不对称单元,现以配合物1为例详细描述结构。在配合物1中,结构单元由1个配位的双酰腙配体、2个苯基以及1个配位的甲醇分子组成。配位原子的2个N来自双酰腙配体的N2和N4,2个O也是来自双酰腙配体的O1和O2,另外2个C分别来自2个苯环上的C29和C35,还有1个甲醇分子的O3参与配位,使得锡原子构成七配位的五角双锥构型,与文献[26]报道类似配合物的几何构型相似。O1、O2、O3、N2、N4占据了赤道平面的5个位置,C29和C35则占据了该平面两侧的轴向位置,轴向C29—Sn1—C35键角为171.61(6)°,相比180°偏离了8.39°,且赤道平面的5个原子与中心锡原子的键长不等,键角也不相等,因此,该配合物中心锡原子为七配位畸变五角双锥构型。
表 2
1 Sn1—O1 0.222 77(12) Sn1—O2 0.224 01(12) Sn1—O3 0.237 46(14) Sn1—N2 0.233 17(14) Sn1—N4 0.230 85(13) Sn1—C29 0.215 01(17) Sn1—C35 0.214 37(17) O1—Sn1—O2 155.90(4) O1—Sn1—O3 77.68(5) O1—Sn1—N2 68.11(4) O1—Sn1—N4 135.62(4) O2—Sn1—N2 135.93(4) O2—Sn1—N4 68.48(5) O2—Sn1—O3 78.23(5) N2—Sn1—O3 145.49(5) N4—Sn1—O3 146.63(5) N4—Sn1—N2 67.53(5) C29—Sn1—N2 96.06(6) C29—Sn1—N4 94.76(6) C29—Sn1—O1 88.48(6) C29—Sn1—O2 89.90(6) C29—Sn1—O3 87.19(6) C35—Sn1—N2 89.90(5) C35—Sn1—N4 92.97(6) C35—Sn1—C29 171.61(6) C35—Sn1—O1 88.28(6) C35—Sn1—O2 89.90(6) C35—Sn1—O3 84.56(6) 2 Sn1—O2 0.228 29(14) Sn1—O4 0.222 95(14) Sn1—O5 0.238 93(16) Sn1—N2 0.230 48(16) Sn1—N3 0.231 64(16) Sn1—C29 0.213 8(2) Sn1—C35 0.213 27(19) O2—Sn1—N2 68.42(5) O2—Sn1—N3 136.20(5) O2—Sn1—O5 81.14(6) O4—Sn1—N2 136.36(5) O4—Sn1—N3 68.63(5) O4—Sn1—O2 155.15(5) O4—Sn1—O5 74.05(6) N2—Sn1—O5 149.55(6) N2—Sn1—N3 67.79(6) N3—Sn1—O5 142.65(6) C29—Sn1—O2 88.02(7) C29—Sn1—O4 89.13(7) C29—Sn1—O5 86.57(7) C29—Sn1—N2 91.66(7) C29—Sn1—N3 93.95(7) C35—Sn1—O2 87.20(7) C35—Sn1—O4 92.48(7) C35—Sn1—O5 86.27(7) C35—Sn1—N2 92.62(7) C35—Sn1—N3 94.00(7) C35—Sn1—C29 171.93(7) 图 2
图 3
双酰腙配体上相邻的原子与Sn形成了3个五元螯合环Sn1—O1—C7—N1—N2、Sn1—N2—C8— C9—N4和Sn1—N4—N3—C10—O2,以锡原子为中心的夹角均不相等,键长也略有差异。结合晶体学数据分析可以看出,该分子中双酰腙配体与Sn配位部分不完全对称,所形成的3个五元螯合环中左右2个环上键参数与中间五元环略有差异。配合物2与配合物1的配位模式类似,中心锡原子也为七配位畸变五角双锥构型。
2.3 热稳定性研究
如图 4、5所示,随着温度的升高,配合物1、2均发生了明显的失重过程。配合物1从40 ℃开始就出现失重现象,配合物2也是在100 ℃之前出现了失重。分析其原因,是2个配合物中存在游离的甲醇分子,导致配合物分子不稳定,容易发生失重,这与X射线单晶衍射测得的结构一致。失去甲醇分子后,配合物1仍持续失重,而配合物2在120~300 ℃之间没有失重,说明配合物2的分子骨架相对稳定;2个配合物的重量最终稳定在约17.82% (1) 和18.53% (2),期间所失去的重量对应的是配合物失去双酰腙配体以及2个苯基,残余物与SnO2的计算含量17.74% (1)及18.44% (2)吻合。上述热分析结果表明配合物2的骨架结构比配合物1稳定。
图 4
图 5
2.4 体外抗癌活性研究
以临床上应用的抗癌药物卡铂为对照品,测定了配合物1、2对NCI-H460(人肺癌细胞)、HepG2(人肝癌细胞)和MCF7(人乳腺癌细胞)的体外抗肿瘤活性。实验结果见表 3。从表中数据可知,配合物1、2对NCI-H460、HepG2和MCF7三种癌细胞均有一定的抑制活性,但是配合物2对3种癌细胞相对更为敏感,其IC50值均比配合物1的要小,并且配合物2对HepG2和MCF7两种癌细胞的IC50值分别为(6.71±0.19) μmol·L-1和(6.71±0.19) μmol·L-1,均小于卡铂对该细胞的IC50值,不过从IC50数值上也可以看出,配合物2对HepG2和MCF7两种癌细胞的抑制效果也仅是略优于卡铂。
表 3
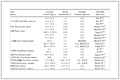 表 3 配合物1、2和卡铂对癌细胞的体外抑制活性Table 3. Inhibition activity of complexes 1, 2 and carboplatin to cancer cell in vitro
表 3 配合物1、2和卡铂对癌细胞的体外抑制活性Table 3. Inhibition activity of complexes 1, 2 and carboplatin to cancer cell in vitroComplex IC50 / (μmol·L-1) NCI-H460 HepG2 MCF7 1 10.03±0.12 8.65±0.09 9.11±0.04 2 7.65±0.13 6.71±0.19 6.71±0.19 Carboplatin 7.26±0.32 7.70±0.25 8.22±0.41 对比1和2的分子结构,发现其差异仅在于配体中苯环上的取代基不同。基于该观察结果,推测可能的结构-活性关系如下:当与锡原子相连接的烃基R相同时,配体上的取代基对配合物的抗癌活性影响较小;另一方面,类salen配体的二苯基锡配合物具有一定的抗癌活性。因此,可以考虑将该类配合物进一步化学优化作为抗癌药物的候选化合物。为此,我们接下来以配合物2为例研究其与DNA的相互作用。
2.5 配合物与DNA作用的紫外可见光谱研究
为了准确表达配合物与DNA相互作用的强度,可以根据下列公式求出两者间的结合常数Kb[27]:cDNA/(εA-εF)=cDNA/(εB-εF)+1/[Kb(εB-εF)],其中εA、εF、εB分别为任意浓度下DNA溶液的摩尔消光系数、自由配合物的摩尔消光系数、配合物被DNA完全键合时的摩尔消光系数。根据方程式线性拟合(图 6插图),通过斜率和截距计算出配合物2的结合常数Kb为1.7×103 L·mol-1;并且该结合常数值与文献[28-29]报道的类似配合物与DNA作用的结合常数大小相近,因此,配合物2与DNA存在结合作用。
图 6
从图 6中可以看出,当配合物2与DNA发生作用时,它们的紫外可见光谱吸收峰表现出了减色和红移现象,减色率为26.7%,红移4 nm,减色越明显表明配合物与DNA相互作用越强[24]。出现这种现象的原因可能是配合物通过嵌入作用与DNA结合后与碱基对发生π-π堆积,配体的π*空轨道与DNA碱基对的π轨道发生耦合导致能级下降,耦合后的π*轨道部分填充电子,使其π-π*跃迁几率减小,从而产生减色效应。上述结果表明配合物2可能通过嵌入作用与双链ct-DNA结合。
2.6 配合物与DNA-EB作用的荧光光谱研究
图 7为不同浓度的配合物2对DNA-EB复合体系荧光光谱的影响。从图上可以看出,随着配合物2浓度的增加,DNA-EB复合物体系的荧光逐渐猝灭,说明配合物2与DNA作用后,同EB竞争DNA的结合位点使EB从DNA分子中游离出来,由此可进一步说明它与DNA发生了嵌入作用,该结论与紫外可见光谱的测试结果一致。
图 7
为了定量地研究配合物与DNA的结合能力,对于荧光强度I和配合物浓度,采用经典Stern-Volmer方程[30]:I0/I=1+KSVccomplex,由曲线拟合推断其作用属于静态猝灭,计算出配合物2与DNA作用的猝灭常数KSV为1.0×105 L·mol-1,比文献[28, 31]报道的结合常数大。KSV的大小定量地反映出配合物与DNA嵌入作用的能力,因此,配合物2与DNA存在较强的嵌入作用。
3. 结论
合成了2个类salen配体的二苯基锡配合物,2个配合物中配体上相邻的原子与Sn形成了3个五元螯合环,中心锡原子均为七配位畸变五角双锥构型。热分析结果表明配合物2的骨架结构比配合物1稳定。体外抗癌活性结果显示,配合物2对癌细胞NCI-H460、HepG2、MCF7表现出略优的抑制活性。利用紫外可见吸收光谱法和荧光光谱法研究配合物2与DNA的相互作用,结果说明配合物2和DNA采用经典的嵌入结合模型。
Supporting information is available at http://www.wjhxxb.cn
-
-
[1]
Rosenberg B, Vancamp L, Trosko J E, Mansour V H. Nature, 1969, 222(5191): 385-386 doi: 10.1038/222385a0
-
[2]
Basu Baul T S, Addepalli M R, Duthie A, Singh P, Koch B, Gildenast H, Englert U, Rojas-León I, Höpfl H. Appl. Organomet. Chem. , 2021, 35(2): e6080
-
[3]
Uddin N, Rashid F, Haider A, Tirmizi S A, Raheel A, Imran M, Zaib S, Diaconescu P L, Iqbal J, Ali S. Appl. Organomet. Chem. , 2021, 35(4): e6165
-
[4]
Hong M, Geng H L, Niu M J, Wang F, Li D C, Liu J F, Yin H D. Eur. J. Med. Chem. , 2014, 86: 550-561 doi: 10.1016/j.ejmech.2014.08.070
-
[5]
Wang H, Hu L, Du W, Tian X H, Zhang Q, Hu Z J, Luo L, Zhou H P, Wu J Y, Tian Y P. ACS Biomater. Sci. Eng. , 2017, 3(5): 836-842 doi: 10.1021/acsbiomaterials.6b00786
-
[6]
Banti C N, Hadjikakou S K, Sismanoglu T, Hadjiliadis N. J. Inorg. Biochem. , 2019, 194: 114-152 doi: 10.1016/j.jinorgbio.2019.02.003
-
[7]
Amir M K, Khan S, Zia ur R, Shah A, Butler I S. Inorg. Chim. Acta, 2014, 423: 14-25 doi: 10.1016/j.ica.2014.07.053
-
[8]
Carraher C E, Roner M R. J. Organomet. Chem. , 2014, 751: 67-82 doi: 10.1016/j.jorganchem.2013.05.033
-
[9]
Ay B, Şahin O, Demir B S, Saygideger Y, López-de-Luzuriaga J M, Mahmoudi G, Safin D A. New J. Chem. , 2020, 44(21): 9064-9072 doi: 10.1039/D0NJ00921K
-
[10]
Srivastava A K, Ghosh S, Jana S, Pal S. Inorg. Chim. Acta, 2018, 483: 329-336 doi: 10.1016/j.ica.2018.08.036
-
[11]
Ramírez-Jiménez A, Luna-García R, Cortés-Lozada A, Hernández S, Ramírez-Apan T, Nieto-Camacho A, Gómez E. J. Organomet. Chem. , 2013, 738: 10-19 doi: 10.1016/j.jorganchem.2013.03.038
-
[12]
Baul T S B, Dutta D, Duthie A, Guchhait N, Rocha B G M, Guedes da Silva M F C, Mokhamatam R B, Raviprakash N, Manna S K. J. Inorg. Biochem. , 2017, 166: 34-48 doi: 10.1016/j.jinorgbio.2016.10.008
-
[13]
Baul T S B, Paul A, Pellerito L, Scopelliti M, Singh P, Verma P, Duthie A, de Vos D, Tiekink E R T. Invest. New Drugs, 2011, 29(2): 285-299 doi: 10.1007/s10637-009-9360-3
-
[14]
Shang X M, Meng X G, Alegria E C B A, Li Q S, da Silva M F C G, Kuznetsov M L, Pombeiro A J L. Inorg. Chem. , 2011, 50(17): 8158-8167 doi: 10.1021/ic200635g
-
[15]
Attanzio A, Ippolito M, Girasolo M A, Saiano F, Rotondo A, Rubino S, Mondello L, Capobianco M L, Sabatino P, Tesoriere L, Casella G. J. Inorg. Biochem. , 2018, 188: 102-112 doi: 10.1016/j.jinorgbio.2018.04.006
-
[16]
Jiang W J, Fan J S, Zhou Q, Zhang F X, Kuang D Z, Tan Y X. Bioorg. Chem. , 2020, 94: 103402 doi: 10.1016/j.bioorg.2019.103402
-
[17]
Sheldrick G M. SHELXL-97, Program for Crystal Structure Refinement, University of Geöttingen, Germany, 1997.
-
[18]
罗波, 余浩田, 刘梦琴, 张复兴, 邝代治, 谭宇星, 蒋伍玖. 无机化学学报, 2019, 35(7): 1212-1220 doi: 10.11862/CJIC.2019.151LUO B, YU H T, LIU M Q, ZHANG F X, KUANG D Z, TAN Y X, JIANG W J. Chinese J. Inorg. Chem. , 2019, 35(7): 1212-1220 doi: 10.11862/CJIC.2019.151
-
[19]
刘骄, 李卓群, 易雨阳, 钟依欣, 余浩田, 谭宇星, 蒋伍玖. 无机化学学报, 2019, 35(12): 2200-2208 doi: 10.11862/CJIC.2019.269LIU J, LI Z Q, YI Y Y, ZHONG Y X, YU H T, TAN Y X, JIANG W J. Chinese J. Inorg. Chem. , 2019, 35(12): 2200-2208 doi: 10.11862/CJIC.2019.269
-
[20]
蒋伍玖, 谭宇星, 邝代治, 张复兴, 刘梦琴. 中国科学: 化学, 2019, 49(8): 1083-1093 https://www.cnki.com.cn/Article/CJFDTOTAL-DXHX200601005.htmJIANG W J, TAN Y X, KUANG D Z, ZHANG F X, LIU M Q. Scientia Sinica: Chimica, 2019, 49(8): 1083-1093 https://www.cnki.com.cn/Article/CJFDTOTAL-DXHX200601005.htm
-
[21]
Deacon G B, Phillips R J. Coord. Chem. Rev. , 1980, 33(3): 227-250 doi: 10.1016/S0010-8545(00)80455-5
-
[22]
Hong M, Yin H D, Zhang X Y, Li C, Yue C H, Cheng S. J. Organomet. Chem. , 2013, 724: 23-31 doi: 10.1016/j.jorganchem.2012.10.031
-
[23]
Salam M A, Hussein M A, Ramli I, Islam M S. J. Organomet. Chem. , 2016, 813: 71-77 doi: 10.1016/j.jorganchem.2016.04.007
-
[24]
Davies A G. Organotin Chemistry. 2nd ed. Weinheim: Wiley-VCH Verlag GmbH & Co. KGaA, 2004.
-
[25]
Pretsch E, Bühlmann P, Badertscher M. Structure Determination of OrganicCompounds. 4th ed. Berlin Heidelberg: Springer-Verlag, 2009.
-
[26]
López-Torres E, Zani F, Mendiola M A. J. Inorg. Biochem. , 2011, 105(5): 600-608 doi: 10.1016/j.jinorgbio.2011.01.014
-
[27]
Pyle A M, Rehmann J P, Meshoyrer R, Kumar C V, Turro N J, Barton J K. J. Am. Chem. Soc. , 1989, 111(8): 3051-3058 doi: 10.1021/ja00190a046
-
[28]
Wang M, Yu F, Jiang W J, Tan Y X, Zhang F X, Kuang D Z. Chin. J. Struct. Chem. , 2020, 39(11): 1965-1972
-
[29]
Zhang Z J, Zeng H T, Liu Y, Kuang D Z, Zhang F X, Tan Y X, Jiang W J. Inorg. Nano-Metal Chem. , 2018, 48(10): 486-494 doi: 10.1080/24701556.2019.1571513
-
[30]
Yan C Q, Zhang J L, Liang T G, Li Q S. Biomed. Pharmacother. , 2015, 71: 119-127 doi: 10.1016/j.biopha.2015.02.027
-
[31]
Zhao Y, Li Z, Li H H, Wang S N, Niu M J. Inorg. Chim. Acta, 2018, 482: 136-143 doi: 10.1016/j.ica.2018.06.008
-
[1]
-
表 1 配合物1和2的晶体学数据
Table 1. Crystallographic data of complexes 1 and 2
Complex 1 2 Empirical formula C44H46N4O6Sn C42H38N4O6Sn Formula weight 845.54 813.45 T / K 273(2) 273(2) Crystal system Triclinic Triclinic Space group P1 P1 a / nm 0.968 97(14) 0.937 12(4) b / nm 1.266 41(18) 1.067 84(5) c / nm 1.765 0(3) 2.005 36(10) α / (°) 106.098(4) 101.575(2) β / (°) 93.394(4) 96.289(2) γ / (°) 96.730(4) 102.982(2) Volume / nm3 2.057 1(5) 1.890 40(15) Z 2 2 Dc / (Mg·m-3) 1.365 1.429 Absorption coefficient / mm-1 0.673 0.729 F(000) 872 832 Crystal size / mm 0.48×0.29×0.28 0.48×0.25×0.13 θ range / (°) 2.92~27.55 3.15~27.51 Limiting indices -12 ≤ h ≤ 12, -16 ≤ k ≤ 16, -22 ≤ l ≤ 22 -12 ≤ h ≤ 12, -13 ≤ k ≤ 13, -26 ≤ l ≤ 26 Reflection collected, unique 43 561, 9 500 (Rint=0.026 4) 39 766, 8 644 (Rint=0.030 1) Completeness 0.998 0.996 Max. and min. transmission 0.834 0 and 0.737 1 0.909 9 and 0.720 6 Data, restraint, parameter 9 500, 0, 507 8 644, 0, 487 Goodness-of-fit on F2 1.091 1.060 Final R indices [I>2σ(I)] R1=0.025 6, wR2=0.064 2 R1=0.030 4, wR2=0.067 2 R indices (all data) R1=0.030 8, wR2=0.066 3 R1=0.037 4, wR2=0.069 5 (Δρ)max, (Δρ)min / (e·nm-3) 373, -403 436, -441 表 2 配合物1和2的部分键长和键角
Table 2. Selected bond lengths (nm) and bond angles (°) of complexes 1 and 2
1 Sn1—O1 0.222 77(12) Sn1—O2 0.224 01(12) Sn1—O3 0.237 46(14) Sn1—N2 0.233 17(14) Sn1—N4 0.230 85(13) Sn1—C29 0.215 01(17) Sn1—C35 0.214 37(17) O1—Sn1—O2 155.90(4) O1—Sn1—O3 77.68(5) O1—Sn1—N2 68.11(4) O1—Sn1—N4 135.62(4) O2—Sn1—N2 135.93(4) O2—Sn1—N4 68.48(5) O2—Sn1—O3 78.23(5) N2—Sn1—O3 145.49(5) N4—Sn1—O3 146.63(5) N4—Sn1—N2 67.53(5) C29—Sn1—N2 96.06(6) C29—Sn1—N4 94.76(6) C29—Sn1—O1 88.48(6) C29—Sn1—O2 89.90(6) C29—Sn1—O3 87.19(6) C35—Sn1—N2 89.90(5) C35—Sn1—N4 92.97(6) C35—Sn1—C29 171.61(6) C35—Sn1—O1 88.28(6) C35—Sn1—O2 89.90(6) C35—Sn1—O3 84.56(6) 2 Sn1—O2 0.228 29(14) Sn1—O4 0.222 95(14) Sn1—O5 0.238 93(16) Sn1—N2 0.230 48(16) Sn1—N3 0.231 64(16) Sn1—C29 0.213 8(2) Sn1—C35 0.213 27(19) O2—Sn1—N2 68.42(5) O2—Sn1—N3 136.20(5) O2—Sn1—O5 81.14(6) O4—Sn1—N2 136.36(5) O4—Sn1—N3 68.63(5) O4—Sn1—O2 155.15(5) O4—Sn1—O5 74.05(6) N2—Sn1—O5 149.55(6) N2—Sn1—N3 67.79(6) N3—Sn1—O5 142.65(6) C29—Sn1—O2 88.02(7) C29—Sn1—O4 89.13(7) C29—Sn1—O5 86.57(7) C29—Sn1—N2 91.66(7) C29—Sn1—N3 93.95(7) C35—Sn1—O2 87.20(7) C35—Sn1—O4 92.48(7) C35—Sn1—O5 86.27(7) C35—Sn1—N2 92.62(7) C35—Sn1—N3 94.00(7) C35—Sn1—C29 171.93(7) 表 3 配合物1、2和卡铂对癌细胞的体外抑制活性
Table 3. Inhibition activity of complexes 1, 2 and carboplatin to cancer cell in vitro
Complex IC50 / (μmol·L-1) NCI-H460 HepG2 MCF7 1 10.03±0.12 8.65±0.09 9.11±0.04 2 7.65±0.13 6.71±0.19 6.71±0.19 Carboplatin 7.26±0.32 7.70±0.25 8.22±0.41 -
 扫一扫看文章
扫一扫看文章
计量
- PDF下载量: 4
- 文章访问数: 2076
- HTML全文浏览量: 348

 下载:
下载:






 下载:
下载:

