

Citation: Xian-Tao JIANG, Xiao-Hui WANG, Pei-Yuan LI, Wei SU. Synthesis, Structure and Photoactivated Anticancer Activity of Ruthenium-Arene Complexes with Curcuminoids[J]. Chinese Journal of Inorganic Chemistry, 2021, 37(3): 431-436. doi: 10.11862/CJIC.2021.047

类姜黄素-芳基钌配合物的合成、结构和光照激活抗癌活性
English
Synthesis, Structure and Photoactivated Anticancer Activity of Ruthenium-Arene Complexes with Curcuminoids
-
Key words:
- ruthenium-arene complexes
- / curcuminoids
- / anticancer activity
- / crystal structure
-
0. 引言
近年来,金属有机配合物因其对不同癌细胞的特异性活性以及良好的细胞毒性而成为科研工作者的研究热点[1⁃2]。其中,钌离子由于其多变的氧化态,在生命体内可以像铁离子一样进入代谢循环,几乎不显毒性,因此钌配合物成为非常有应用潜力的新型抗癌药物[3]。例如[HIm][trans-RuCl4(DMSO) (Im)](NAMI-A)和[ImH][trans-RuCl4(Im)2](KP1019)已经成功进入抗肿瘤临床试验[4-6]。此外,分子式为[(η6-arene)Ru(X)(Y)(Z)]的半三明治型芳基钌配合物由于其特殊的分子构型及其在抗癌研究中的作用,也引起了越来越多的关注。如Sadler课题组报道的[(η6-bip)Ru(en)Cl]PF6(en=乙二胺)表现出优异的肿瘤细胞抑制活性[7-8],Dyson课题组报道的[(η6-cymene) Ru(PTA)Cl2](PTA=1,3,5-三氮杂-7-磷金刚烷)则表现出良好的抗转移活性[9-10]。在这些配合物中,配体X、Y和Z的性质和结构对配合物的抗癌活性起着至关重要的作用[11-16]。
作为一类β-二酮配体,姜黄素及其衍生物(cur-cuminoids,Curc)以其抗炎、抗菌和抗肿瘤等广谱的生物活性而受到人们的广泛关注[17]。Caruso课题组报道了系列含类姜黄素配体的芳基钌配合物[(η6-cymene)Ru(Curc)Cl],并发现这些配合物对肿瘤细胞有很好的抑制活性[18]。Dyson课题组在芳基钌-类姜黄素配合物中引入PTA配体,获得了具有良好抗癌选择性的芳基钌配合物[(η6-cymene)Ru(Curc)(PTA)] PF6[19]。此外,类姜黄素及金属配合物的光谱和光化学性质具有一个重要特性:在波长为410~430 nm的光谱有强烈的吸收[20]。这一特性使得此类化合物具备光敏性,可利用光照来增强其抗癌活性[21]。Kondaiah课题组报道了含姜黄素配体的铂配合物[Pt(Curc)(NH3)2]NO3,其在光照下细胞毒性比避光条件下提高13倍[22]。Renfrew课题组报道了一系列可在有氧和无氧环境下激活的含姜黄素配体的钴配合物,其细胞光毒性比避光条件下提高20倍[23]。为了延续本课题组先前对芳基钌-类姜黄素配合物的探索,我们合成了3种新型的芳基钌-类姜黄素-PTA配合物[24],通过核磁共振、质谱、单晶衍射等方法表征了它们的结构,通过MTT法研究其抗癌活性,并利用光照对其细胞光毒性进行了研究。
1. 实验部分
1.1 试剂与仪器
实验所用溶剂均采用国产分析纯试剂并在使用前进行纯化。[(p-cymene)RuCl2]2和其他试剂购自百灵威试剂公司, 类姜黄素配体(L1~L3)均通过文献方法制备[24]。1H NMR采用Bruker AV-600(德国)核磁共振波谱仪以600 MHz的频率测定;HR-ESI-MS使用Waters UPLC XEVO G2 TOF质谱仪测定;C、H、N元素分析使用Elementar Vario EL Cube元素分析仪测定;UV-Vis使用Cary 100紫外可见分光光度计(澳大利亚安捷伦科技有限公司)测定;荧光光谱使用Thermo荧光光谱仪(美国)测定;单晶结构使用Bruker SMART CCD X射线单晶衍射仪测定。
1.2 配合物1~3的合成
配合物1~3的合成过程如Scheme 1所示。
Scheme 1
1.2.1 配合物[(η6-p-cymene)Ru(L1) (PTA)]PF6 (1)的合成
将[(η6-p-cymene)RuCl2]2(31 mg,0.05 mmol)、配体L1(27.6 mg,0.1 mmol)和NaOEt(10.2 mg,0.15 mmol)溶解在6 mL乙醇中。室温搅拌2 h,加入AgPF6(25.7 mg,0.1 mmol)后继续搅拌2 h。过滤以除去AgCl沉淀,在滤液中加入PTA(15.7 mg,0.1 mmol),室温搅拌24 h,析出暗红色固体,通过CH2Cl2/正己烷重结晶进行进一步纯化(50.0 mg,产率62%)。元素分析(%,括号内为按C35H41F6N3O2P2Ru·1/4CH2Cl2计算值):C 50.94(50.77),H 4.99(5.02),N 5.04(5.04)。1H NMR (600 MHz,DMSO - d6):δ 7.685(d,J=6.0 Hz,4H),7.477~7.425(m,8H),6.903(d,J=16.2 Hz,2H),6.133 (dd,J=32.4,5.4 Hz,4H),5.950(s,1H),4.474(dd,J= 28.8,12.6 Hz,6H),4.138(s,6H),2.690(dd,J=13.8,6.6 Hz,1H),2.038(s,3H),1.300(d,J=6.6 Hz,6H)。HR⁃ESI⁃MS(DMSO):[1-PF6-]+ m/z实测值(理论值):668.199 8(668.199 0)。
1.2.2 [Ru(η6-p-cymene)(L2)(PTA)]PF6 (2)的合成
合成步骤同1。产量56 mg,产率66%。元素分析(%, 括号内为按C35H39F8N3O2P2Ru·H2O计算值):C 48.55(48.50),H 4.89(4.77),N 4.99(4.85)。1H NMR (600 MHz,DMSO-d6):δ 7.766(dd,J=8.4,5.4 Hz,4H),7.440(d,J=16.2 Hz,2H),7.300(t,J=9.0 Hz,4H),6.861 (d,J=15.9 Hz,2H),6.123(dd,J=28.8,5.4 Hz,4H),5.903(s,1H),4.447(q,J=26.4,12.6 Hz,6H),4.128(s,6H),2.683~2.637(m,1H),2.028(s,3H),1.289(d,J=6.6 Hz,6H)。HR-ESI-MS(DMSO):[1-PF6-]+ m/z实测值(理论值):704.179 6(704.180 1)。
1.2.3 [Ru(η6-p-cymene)(L3)(PTA)]PF6 (3)的合成
合成步骤同1。产量43 mg,产率49%。元素分析(%, 括号内为按C37H45F6N3O4P2Ru·5/4H2O计算值):C 49.50(49.64),H 5.10(5.35),N 4.92(4.69),1H NMR (600 MHz,DMSO-d6):δ 7.631(d,J=6.4 Hz,4H),7.409 (d,J=15.6 Hz,2H),7.016(d,J=9.0 Hz,4H),6.742(d,J=15.6 Hz,2H),6.133(dd,J=34.2,5.4 Hz,4H),5.845 (s,1H),4.440(q,J=22.8,12.6 Hz,6H),4.120(s,6H),3.819(s,6H),2.687~2.641(m,1H),2.030(s,3H),1.293 (d,J=6.6 Hz,6H)。HR-ESI-MS(DMSO):[1-PF6-]+ m/z实测值(理论值):728.220 1(728.220 2)。
1.3 结构测定
配合物1~3的单晶测试是在293 K下用石墨单色化Mo Kα射线(λ=0.071 073 nm)于单晶衍射仪上,进行衍射点数据收集。利用直接法解出结构,并混合加氢,氢原子采用各向同性热参数。非氢原子采用各向异性热参数。结构经全矩阵最小二乘法修正,用SHELXL2016[25-26]和OLEX.2程序包分别进行晶体结构解析和结构修正。配合物1~3的单晶结构数据见表 1,配合物1~3的部分键长、键角数据见表 2。
表 1
Complex 1 2 3 Formula C35H41F6N3O2P2Ru C35H39F8N3O2P2Ru C37H45F6N3O4P2Ru Formula weight 812.72 848.70 875.79 Crystal system Monoclinic Monoclinic Triclinic Space group C2/c C2/c P 6(9) 1(12) 1 5(3) a/ nm 1.961 2.623 1.328 b/ nm 1.762 2(9) 1.753 4(12) 1.333 6(3) c/ nm 2.203 5(11) 1.934 5(13) 1.350 2(3) α/(°) 104.806(3) β/(°) 101.27(5) 124.681(14) 118.462(3) γ/(°) 91.598(3) V/ nm3 7.470(6) 7.317(8) 2.001 3(8) Z 8 8 2 Dc/ (g·cm-3) 1.445 1.541 1.453 F(000) 3 328 3 456 902 θ range / (°) 2.54~52.58 3~50.06 3.2~50.7 Reflection collected 42 927 38 967 20 475 Reflection independent 7 343 6 465 7 289 GOF 1.147 1.032 1.078 R1, wR2 [I≥2σ(I)] 0.079 3, 0.236 5 0.037 0, 0.100 6 0.056 5, 0.135 3 R1, wR2 (all data) 0.096 0, 0.263 3 0.043 9, 0.108 0 0.073 4, 0.153 7 表 2
Complex 1 2 3 Ru1-centroid 0.170 71(9) 0.173 31(8) 0.170 95(3) Ru1-P1 0.231 7(2) 0.231 7(12) 0.232 6(12) Ru1-O1 0.206 7(4) 0.207 4(2) 0.205 6(3) Ru1-O2 0.207 6(4) 0.207 6(2) 0.207 0(3) O1-C2 0.127 2(7) 0.127 3(4) 0.129 3(6) O2-C2' 0.127 0(7) 0.128 1(4) 0.128 8(6) C1-C2 0.140 8(14) 0.149 5(6) 0.150 0(7) C1-C2' 0.140 0(12) 0.141 5(5) 0.141 4(7) O1-Ru1-O2 88.76(16) 88.90(1) 87.83(13) O1-Ru1-P1 85.77(14) 86.15(7) 86.71(1) O2-Ru1-P1 85.95(13) 86.06(7) 85.70(9) CCDC:1514601,1;1514600,2;1514603,3。
1.4 配合物的抗癌活性
本研究所使用的人肝癌细胞(HepG2)来自广西医科大学实验中心。细胞在含10% 的血清培养基RPMI-1640中生长。用MTT法测定配合物对癌细胞体外抗增殖活性:取对数期生长的癌细胞,配成细胞悬液,加入96孔板,每孔(200 μL)1×104~3×104个细胞,置培养箱内培养24 h; 采用MTT法,每孔加入1 μL不同浓度的药物,控制药物终浓度分别为10、20、30、50、60、80 μmol·L-1,在培养箱中培养4 h后,癌细胞在λ>400 nm,功率密度为30 mW·cm-2的条件光照30 min,继续在培养箱中培养24 h。每孔加入20 μL(5 mg·mL-1) MTT,再置于培养箱中培养4 h,吸掉上清液,每孔加入100 μL的DMSO,置于摇床上低速震荡,10 min后使用酶标仪上测量492 nm波长处OD值。每种药物重复3次实验,每次做3个复孔。计算配合物对癌细胞的IC50值。
2. 结果与讨论
2.1 合成与表征
配合物1~3均采用相同的方法合成:在室温下将[(η6-p-cymene)RuCl2]2与相应的类姜黄素配体反应后,加入AgPF6除去Cl-,再加入PTA进一步反应合成得到。用核磁共振波谱、高分辨质谱、元素分析等手段对1~3进行了表征。其中,高分辨质谱实验测得配合物1~3的m/z峰值分别为668.199 8、704.179 6和728.220 1,相对应的正离子分别为[(η6-p-cymene)Ru(L1)(PTA)]+、[(η6-p-cymene)Ru(L2)(PTA)]+和[(η6-p-cymene)Ru(L3)(PTA)]+,与配合物1~3的阳离子相吻合。
将配合物1~3配成浓度为20 μmol·L-1的DMSO溶液,研究其UV-Vis光谱。从图 1可以看到,这些配合物在310~510 nm区域有明显的吸收,该吸收峰主要归因于配体以及金属- 配体电荷转移(1MLCT)[27]。配合物1和2的吸收光谱相似,其最大吸收峰位于375 nm,配合物3的最大吸收峰位于411 nm,相对于1和2明显红移。这是由于配体L3端位上的供电子基团OCH3导致。
图 1
2.2 配合物的晶体结构
配合物1~3的单晶结构如图 2~4所示。配合物1和2属于单斜晶系的C2/c空间群,配合物3的晶体属于三斜晶系P1空间群。3个配合物具有相似结构,其中心金属钌(Ⅱ)离子与甲基异丙基苯配体中的苯环以η6形式配位,与类姜黄素配体以O,O螯合配位,与PTA配体中的P原子以单齿配位,形成六配位八面体结构的一价阳离子。甲基异丙基苯配体中的苯环中心与钌离子之间的距离分别为0.170 71(9)、0.173 31(8)、0.170 95(3) nm。另外3个配位键键长为Ru1—P1 0.231 7~0.232 6 nm、Ru1—O1 0.205 6~0.206 7 nm、Ru1—O2 0.207 0~0.207 6 nm,表明3个配合物的结构非常相似。C1—C2和C1—C2'的键长在0.140 8~0.150 0 nm范围,该长度处于单键键长和双键键长之间,这是由配体中β-二酮的部分形成去质子化螯合配体后主要以(—O—C—C—O—)形式共振而导致。围绕金属钌离子的键角为O1—Ru1—O2 87.83° ~88.76°、O1—Ru1—P1 85.77°~86.71°、O2—Ru1—P1 85.95°~86.06°,与之前报道的类似配合物数值接近[24]。
图 2
图 3
图 4
2.3 配合物的细胞活性测试
类姜黄素-芳基钌配合物1~3对HepG2人肝癌细胞的体外抗肿瘤活性见表 3。结果显示,在避光条件下,配合物1和2对HepG2细胞均未表现出抗肿瘤活性,配合物3对HepG2细胞表现出一定抗肿瘤活性,IC50值为(60.3±1.1) μmol·L-1。显然,相对于吸电子基团(配合物1和2中的H和F原子),类姜黄素配体端位的供电子基团(配合物3中的—OCH3)对此类配合物的HepG2细胞增殖抑制活性影响更为正面。使用λ>400 nm的光照射30 min后,配合物1仍未显示出抗肿瘤活性,但配合物2和3对HepG2细胞的增殖抑制活性得到明显提高,其IC50值分别降低为(60.1±1.0) μmol·L-1和(45.0±6.1) μmol·L-1。这说明利用光照作用,可以有效提高类姜黄素-芳基钌配合物的抗肿瘤活性,这可能是由于配合物在光照后产生活性氧[22],从而提高了配合物的细胞毒性。因此,虽然这3个配合物对HepG2细胞的增殖抑制活性较为温和,但是本研究对于此类配合物的构效关系研究和提高其使用效率具有一定的参考价值。
表 3
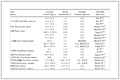 表 3 配合物1~3对人肝癌细胞(HepG2)的IC50值(λ>400 nm)Table 3. IC50 values (λ>400 nm) of 1~3 against HepG2 cancer cell lines
表 3 配合物1~3对人肝癌细胞(HepG2)的IC50值(λ>400 nm)Table 3. IC50 values (λ>400 nm) of 1~3 against HepG2 cancer cell linesComplex IC50, dark/
(μmol·L-1)IC50, light/
(μmol·L-1)PI* 1 > 100 > 100 - 2 > 100 60.1±1.0 1.7 3 60.3±1.1 45.0±6.1 1.3 *PI=IC50, dark/IC50, light 3. 结论
设计、合成了3种新型类姜黄素-芳基钌配合物1~3。并通过单晶X射线衍射实验,对比研究了这3个配合物的结构。在避光条件下,配合物1和2对HepG2人肝癌细胞不显活性,而配合物3表现出一定的活性,原因可能是相对于吸电子基团的H原子和F原子,类姜黄素配体端位苯环上的供电子基团—OCH3更有利于配合物对HepG2细胞的增殖抑制活性。光照后(λ>400 nm),除配合物1外,2和3对HepG2细胞的增殖抑制活性都有明显提高,说明光照可以有效提高此类配合物的抗肿瘤活性。本研究为进一步设计合成新型高效抗癌芳基配合物提供了一定的理论基础。
-
-
[1]
Murray B S, Babak M V, C G Hartinger, Dyson P. Coord. Chem. Rev., 2016, 306: 86-114 doi: 10.1016/j.ccr.2015.06.014
-
[2]
Furrer J, Süss-Fink G. Coord. Chem. Rev., 2016, 309: 36-50 doi: 10.1016/j.ccr.2015.10.007
-
[3]
赵雅晨, 李季, 张培培, 刘姝娴, 魏代娜, 苏志, 钱勇, 王飞利, Sadler P J, 刘红科. 高等学校化学学报, 2019, 40(1): 30-40 https://www.cnki.com.cn/Article/CJFDTOTAL-JFJY202001002.htmZHAO Y C, LI J, ZHANG P P, LIU S X, WEI D N, SU Z, QIAN Y, WANG F L, Sadler P J, LIU H K. Chem. J. Chinese Universities, 2019, 40(1): 30-40 https://www.cnki.com.cn/Article/CJFDTOTAL-JFJY202001002.htm
-
[4]
Thompson D S, Weiss G J, Jones S F, Burris H A, Ramanathan R K, Infante J R, Ogden A, von Hoff D D. J. Clin. Oncol., 2012, 30(S15): Abstr. 3033 doi: 10.1200/jco.2012.30.15_suppl.3033
-
[5]
Kubanik M, Kandioller W, Kim K W, Anderson R F, Klapproth E, Jakupec M A, Roller A, Söhnel T, Keppler B K, Hartinger C G. Dalton Trans., 2016, 45: 13091-13103 doi: 10.1039/C6DT01110A
-
[6]
Trondl R, Heffeter P, Kowol C R, Jakupec M A, Berger W, Keppler B K. Chem. Sci., 2014, 5: 2925-2932 doi: 10.1039/C3SC53243G
-
[7]
Morris R E, Aird R E, Socorro P S, Chen H M, Cummings J, Hughes N D, Parsons S, Parkin A, Boyd G, Jodrell D I, Sadler P J. J. Med. Chem., 2001, 44: 3616-3621 doi: 10.1021/jm010051m
-
[8]
Chen H M, Parkinson J A, Parsons S, Coxall R A, Gould R O, Sadler P J. J. Am. Chem. Soc., 2002, 124(12): 3064-3082 doi: 10.1021/ja017482e
-
[9]
Scolaro C, Bergamo A, Brescacin L, Delfino R, Cocchietto M, Laurenczy G, Geldbach T J, Sava G, Dyson P J. J. Med. Chem., 2005, 48: 4161-4171 doi: 10.1021/jm050015d
-
[10]
Chatterjee S, Kundu S, Bhattacharyya A, Hartinger C G, Dyson P J. J. Biol. Inorg. Chem., 2008, 13: 1149-1155 doi: 10.1007/s00775-008-0400-9
-
[11]
Batchelor L K, Paunescu E, Soudani M, Scopelliti R, Dyson P J. Inorg. Chem., 2017, 56(16): 9617-9633 doi: 10.1021/acs.inorgchem.7b01082
-
[12]
Ma L L, Ma R, Wang Z G, Yiu S M, Zhu G Y. Chem. Commun., 2016, 52(71): 10735-10738 doi: 10.1039/C6CC04354B
-
[13]
Prior T J, Savoie H, Boyle R W, Murray B S. Organometallics, 2018, 37(3): 294-297 doi: 10.1021/acs.organomet.7b00868
-
[14]
Caruso F, Pettinari R, Rossi M, Monti E, Gariboldi M B, Marchetti F, Pettinari C, Caruso A, Ramani M V, Subbaraju G V. J. Inorg. Biochem., 2016, 162: 44-51 doi: 10.1016/j.jinorgbio.2016.06.002
-
[15]
Ma L L, Lin X D, Li C, Xu Z F, Chan C Y, Tse M K, Shi P, Zhu G Y. Inorg. Chem., 2018, 57(5): 2917-2924 doi: 10.1021/acs.inorgchem.8b00053
-
[16]
Paunescu E, Soudani M, Martin P, Scopelliti R, Bello M L, Dyson P J. Organometallics, 2017, 36(17): 3313-3321 doi: 10.1021/acs.organomet.7b00468
-
[17]
Lei X L, Su W, Li P Y, Xiao Q, Huang S, Qian Q Q, Huang C S, Qian D N, Lan H X. Polyhedron, 2014, 81: 614-618 doi: 10.1016/j.poly.2014.07.019
-
[18]
Caruso F, Rossi M, Benson A, Opazo C, Freedman D, Monti E, Gariboldi M B, Shaulky J, Marchetti F, Pettinari R. J. Med. Chem., 2012, 55: 1072-1081 doi: 10.1021/jm200912j
-
[19]
Pettinari R, Pettinari C, Mahetti F, Clavel C M, Scopelliti R, Dyson P J. Organometallics, 2014, 33(14): 3709-3715 doi: 10.1021/om500317b
-
[20]
Banerjee S, Chakravarty A R. Acc. Chem. Res., 2015, 48: 2075-2083 doi: 10.1021/acs.accounts.5b00127
-
[21]
Zhang J F, Liang Y C, Lin X D, Zhu X Y, Yan L, Li S L, Yang X, Zhu G Y, Rogach A L, Yu P K N, Shi P, Tu L C, Chang C C, Zhang X H, Chen Z F, Zhang W J, Lee C S. ACS Nano, 2015, 9: 9741-9756 doi: 10.1021/acsnano.5b02513
-
[22]
Mitra K, Gautam S, Kondaiah P, Chakravarty A R. Angew. Chem. Int. Ed., 2015, 54: 13989-13993 doi: 10.1002/anie.201507281
-
[23]
Renfrew A K, Bryce N S, Hambley T. Chem. Eur. J., 2015, 21: 1522415234 doi: 10.1002/chem.201502702
-
[24]
Li P Y, Su W, Lei X L, Xiao Q, Huang S. Appl Organometal Chem., 2017, 31: e3685 doi: 10.1002/aoc.3685
-
[25]
Sheldrick G M. Acta Crystallogr. Sect. C, 2015, 71: 3-8 doi: 10.1107/S2053229614024218
-
[26]
Sheldrick G M. Acta Crystallogr. Sect. A, 2008, 64: 112-122 doi: 10.1107/S0108767307043930
-
[27]
Su W, Zhou Q, Huang Y M, Huang Q Y, Huo L N, Xiao Q, Huang S, Huang C S, Chen R, Qian Q Q, Liu L F, Li P Y. Appl. Organometal Chem., 2013, 27: 307-312 doi: 10.1002/aoc.2977
-
[1]
-
表 1 配合物1~3的晶体数据
Table 1. Crystal data collection for 1~3
Complex 1 2 3 Formula C35H41F6N3O2P2Ru C35H39F8N3O2P2Ru C37H45F6N3O4P2Ru Formula weight 812.72 848.70 875.79 Crystal system Monoclinic Monoclinic Triclinic Space group C2/c C2/c P 6(9) 1(12) 1 5(3) a/ nm 1.961 2.623 1.328 b/ nm 1.762 2(9) 1.753 4(12) 1.333 6(3) c/ nm 2.203 5(11) 1.934 5(13) 1.350 2(3) α/(°) 104.806(3) β/(°) 101.27(5) 124.681(14) 118.462(3) γ/(°) 91.598(3) V/ nm3 7.470(6) 7.317(8) 2.001 3(8) Z 8 8 2 Dc/ (g·cm-3) 1.445 1.541 1.453 F(000) 3 328 3 456 902 θ range / (°) 2.54~52.58 3~50.06 3.2~50.7 Reflection collected 42 927 38 967 20 475 Reflection independent 7 343 6 465 7 289 GOF 1.147 1.032 1.078 R1, wR2 [I≥2σ(I)] 0.079 3, 0.236 5 0.037 0, 0.100 6 0.056 5, 0.135 3 R1, wR2 (all data) 0.096 0, 0.263 3 0.043 9, 0.108 0 0.073 4, 0.153 7 表 2 配合物1~3的键长(nm)和键角(°)
Table 2. Selected bond lengths (nm) and angles (°) in complexes 1~3
Complex 1 2 3 Ru1-centroid 0.170 71(9) 0.173 31(8) 0.170 95(3) Ru1-P1 0.231 7(2) 0.231 7(12) 0.232 6(12) Ru1-O1 0.206 7(4) 0.207 4(2) 0.205 6(3) Ru1-O2 0.207 6(4) 0.207 6(2) 0.207 0(3) O1-C2 0.127 2(7) 0.127 3(4) 0.129 3(6) O2-C2' 0.127 0(7) 0.128 1(4) 0.128 8(6) C1-C2 0.140 8(14) 0.149 5(6) 0.150 0(7) C1-C2' 0.140 0(12) 0.141 5(5) 0.141 4(7) O1-Ru1-O2 88.76(16) 88.90(1) 87.83(13) O1-Ru1-P1 85.77(14) 86.15(7) 86.71(1) O2-Ru1-P1 85.95(13) 86.06(7) 85.70(9) 表 3 配合物1~3对人肝癌细胞(HepG2)的IC50值(λ>400 nm)
Table 3. IC50 values (λ>400 nm) of 1~3 against HepG2 cancer cell lines
Complex IC50, dark/
(μmol·L-1)IC50, light/
(μmol·L-1)PI* 1 > 100 > 100 - 2 > 100 60.1±1.0 1.7 3 60.3±1.1 45.0±6.1 1.3 *PI=IC50, dark/IC50, light -
 扫一扫看文章
扫一扫看文章
计量
- PDF下载量: 9
- 文章访问数: 2484
- HTML全文浏览量: 334

 下载:
下载:




 下载:
下载:

